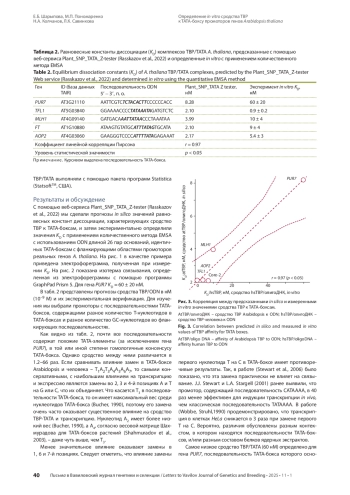
Для инициации транскрипции РНК-полимеразой II с ТАТА-содержащих промоторов необходима сборка транскрипционного комплекса, начинающаяся со взаимодействия ТВР (TATA binding protein) или TFIID, в состав которого он входит, с ТАТА-боксом, и присоединения к ним других базальных факторов транскрипции. Изучению взаимодействия ТВР с ТАТА-боксами и ТАТА-подобными элементами млекопитающих посвящено большое количество работ, увеличивающееся с обнаружением влияния однонуклеотидных замен (SNP) в ТАТА-последовательностях на фенотипические проявления, в том числе на связь с различными заболеваниями человека. Взаимодействие ТВР с ТАТА-боксами растений, в частности Аrabidopsis thaliana, практически не изучалось, за исключением единичных ранних работ. Широкомасштабное предсказание промоторных последовательностей и входящих в них сайтов связывания транскрипционных факторов с помощью различных инструментов in silico успешно используется благодаря достижениям в транскриптомных технологиях и секвенировании геномов довольно многих видов растений ( A. thaliana, рис, томат, свекла, картофель, пшеница, хлопчатник и др.). Однако предсказанные регуляторные последовательности могут быть функциональными (а могут и не быть), и необходима экспериментальная верификация вклада потенциального сайта связывания фактора транскрипции в активность промотора для подтверждения его функциональности. В данной работе применяется количественный метод задержки ДНК в геле для определения сродства ТВР к ТАТА-боксам промоторов генов A. thaliana и его сравнения с предсказанным с помощью веб-сервиса Plant_SNP_TATA_Z-tester значением. Для изучения мы использовали гены A. thaliana PUR7, TFL1, MLH1, FT, AOP2, транскрибируемые в разных органах растения. Выявлено, что олигодезоксирибонуклеотиды, идентичные последовательностям ТАТА-боксов с фланкирующими их нуклеотидами генов А. thaliana, имеют сродство к ТВР, различающееся до 66 раз. Фланкирующие последовательности ТАТА-боксов промоторов рассмотренных генов А. thaliana имеют более низкое содержание GC-нуклеотидов во фланках (на 23 %) по сравнению с генами человека. Эксперименты показали, что для предсказанных с помощью Plant_SNP_TATA_Z-tester равновесных констант диссоциации K D и их экспериментальных значений, выраженных в нМ, коэффициент линейной корреляции ( r ) = 0.97 при p < 0.05. Полученные результаты указывают на надежность in silico оценки сродства ТВР Arabidopsis к промоторам генов этого растения с помощью сервиса Plant_SNP_TATA_Z-tester.
Идентификаторы и классификаторы
Для инициации транскрипции с помощью РНК-полимеразы II всем эукариотам требуется сборка базального аппарата транскрипции на кор-промоторе – области, расположенной в районе примерно (–50, +50) пар нуклеотидов выше и ниже сайта инициации транскрипции (transcription start site, TSS) (Hampsey, 1998; Sandelin et al., 2007; Juven-Gershona, Kadonaga, 2010; Kadonaga, 2012). Кор-промоторы часто содержат консервативные элементы ДНК, распознаваемые компонентами базального транскрипционного аппарата, – общими (general, basal) факторами транскрипции: TFIID, TFIIB, TFIIA, TFIIF, TFIIE и TFIIH (Sandelin et al., 2007). Наиболее хорошо описан элемент ДНК кор-промотора – ТАТАбокс, который распознается ТАТА-связывающим белком (TATA binding protein, ТВР). TATA-бокс представляет собой АТ-богатую последовательность, расположенную примерно на 25–35 пар оснований выше TSS почти у всех эукариот (Burley, Roeder, 1996). Рекрутирование ТВР и ассоциированных с ним факторов, являющихся частью основного фактора транскрипции TFIID, направляет сборку преинициаторного комплекса (preinitiation complex, PIC) на кор-промоторе. Это строго регулируемый процесс, обеспечивающий точную инициацию транскрипции.
Список литературы
1. Bucher P. Weight matrix descriptions of four eukaryotic RNA polymerase II promoter elements derived from 502 unrelated promoter sequences. J Mol Biol. 1990;212(4):563-578. 10.1016/0022 2836(90)90223-9. DOI: 10.1016/00222836(90)90223-9
2. Burley S.K., Roeder R.G. Biochemistry and structural biology of transcription factor IID (TFIID). Annu Rev Biochem. 1996;65:769-799. DOI: 10.1146/annurev.bi.65.070196.004005
3. Burow M., Atwell S., Francisco M., Kerwin R.E., Halkier B.A., Kliebenstein D.J. The glucosinolate biosynthetic gene AOP2 mediates feedback regulation of jasmonic acid signaling in Arabidopsis. Mol Plant. 2015;8(8):1201-1212. DOI: 10.1016/j.molp.2015.03.001
4. Cerise M., da Silveira Falavigna V., Rodríguez-Maroto G., Signol A., Severing E., Gao H., van Driel A., Vincent C., Wilkens S., Iacobini F.R., Formosa-Jordan P., Pajoro A., Coupland G. Two modes of gene regulation by TFL1 mediate its dual function in flowering time and shoot determinacy of Arabidopsis. Development. 2023;150(23):dev202089. DOI: 10.1242/dev.202089
5. Corbesier L., Vincent C., Jang S., Fornara F., Fan Q., Searle I., Giakountis A., Farrona S., Gissot L., Turnbull C., Coupland G. FT protein movement contributes to long-distance signaling in floral induction of Arabidopsis. Science. 2007;316(5827):1030-1033. 10.1126/ science.1141752. DOI: 10.1126/science.1141752
6. Das B. Glucosinolate biosynthesis: role of MAM synthase and its perspectives. Biosci Rep. 2021;41(10):BSR20211634. 10.1042/ BSR20211634. DOI: 10.1042/BSR20211634
7. Das S., Bansal M. Variation of gene expression in plants is influenced by gene architecture and structural properties of promoters. PLoS One. 2019;14(3):e0212678. DOI: 10.1371/journal.pone.0212678 EDN: NGZSHX
8. Dikstein R. The unexpected traits associated with core promoter elements. Transcription. 2011;2(5):201-206. DOI: 10.4161/trns.2.5.17271
9. Dion E., Li L., Jean M., Belzile F. An Arabidopsis MLH1 mutant exhibits reproductive defects and reveals a dual role for this gene in mitotic recombination. Plant J. 2007;51(3):431-440. 10.1111/ j.1365-313X.2007.03145.x. DOI: 10.1111/j.1365-313X.2007.03145.x
10. Drachkova I.A., Ponomarenko P.M., Arshinova T.V., Ponomarenko M.P., Suslov V.V., Savinkova L.K., Kolchanov N.A. In vitro examining the existing prognoses how TBP binds to TATA with SNP associated with human diseases. Health. 2011;3(9):577-583. 10.4236/ health.2011.39099. DOI: 10.4236/health.2011.39099
11. Faiger H., Ivanchenko M., Cohen I., Haran T.E. TBP flanking sequences: asymmetry of binding, long-range effects and consensus sequences. Nucleic Acids Res. 2006;34:104-119. DOI: 10.1093/nar/gkj414 EDN: ITYGVV
12. Garcia-Hernandez M., Berardini T.Z., Chen G., Crist D., Doyle A., Huala E., Knee E., Lambrecht M., Miller N., Mueller L.A., Mundodi S., Reiser L., Rhee S.Y., Scholl R., Tacklind J., Weems D.C., Wu Y., Xu I., Yoo D., Yoon J., Zhang P. TAIR: a resource for integrated Arabidopsis data. Funct Integr Genomics. 2002;2(6):239-253. DOI: 10.1007/s10142-002-0077-z
13. Goretti D., Silvestre M., Collani S., Langenecker T., Méndez C., Madueño F., Schmid M. TERMINAL FLOWER1 functions as a mobile transcriptional cofactor in the shoot apical meristem. Plant Physiol. 2020;182(4):2081-2095. DOI: 10.1104/pp.19.00867 EDN: VQXPTM
14. Hampsey M. Molecular genetics of the RNA polymerase II general transcriptional machinery. Microbiol Mol Biol Rev. 1998;62:465-503. DOI: 10.1128/MMBR.62.2.465-503.1998
15. Holdsworth M.J., Grierson C., Schuch W., Bevan M. DNA-binding properties of cloned TATA-binding protein from potato tubers. Plant Mol Biol. 1992;19:455-464. DOI: 10.1007/BF00023393
16. Iwataki N., Hoya A., Yamazaki K. Restoration of TATA-dependent transcription in a heat-inactivated extract of tobacco nuclei by recombinant TATA-binding protein (TBP) tobacco. Plant Mol Biol. 1997;34:69-79. :1005759521285. DOI: 10.1023/A
17. Juven-Gershona T., Kadonaga J.T. Regulation of gene expression via the core promoter and the basal transcriptional machinery. Dev Biol. 2010;339(2):225-229. DOI: 10.1016/j.ydbio.2009.08.009 EDN: NYZCCN
18. Kadonaga J.T. Perspectives on the RNA polymerase II core promoter. Wiley Interdiscip Rev Dev Biol. 2012;1(1):40-51. DOI: 10.1002/wdev.21
19. Lv X., Zeng X., Hu H., Chen L., Zhang F., Liu R., Liu Y., Zhou X., Wang C., Wu Z. Structural insights into the multivalent binding of the Arabidopsis FLOWERING LOCUS T promoter by the CO-NF-Y master transcription factor complex. Plant Cell. 2021;33(4):1182-1195. DOI: 10.1093/plcell/koab016 EDN: LLCQGW
20. Marks R.A., Hotaling S., Frandsen P.B., VanBuren R. Representation and participation across 20 years of plant genome sequencing. Nat Plants. 2021;7(12):1571-1578. doi 0.1038/s41477-021-01031-8.
21. Mogno I., Vallania F., Mitra R.D., Cohen B.A. TATA is a modular component of synthetic promoters. Genome Res. 2010;20(10):1391-1397. DOI: 10.1101/gr.106732.110
22. Morey C., Mookherjee S., Rajasekaran G., Bansal M. DNA free energybased promoter prediction and comparative analysis of Arabidopsis and rice genomes. Plant Physiol. 2011;156(3):1300-1315. DOI: 10.1104/p.p.110.167809
23. Mukumoto F., Hirose S., Imaseki H., Yamazaki K.-I. DNA sequence requirement of a TATA element-binding protein from Arabidopsis for transcription in vitro. Plant Mol Biol. 1993;23:995-1003. DOI: 10.1007/BF00021814
24. Patikoglou G.A., Kim J.L., Sun L., Yang S.H., Kodadek T., Burley S.K. TATA element recognition by the TATA box-binding protein has been conserved throughout evolution. Genes Dev. 1999;13(24):3217-3230. DOI: 10.1101/gad.13.24.3217
25. Ponomarenko M., Rasskazov D., Arkova O., Ponomarenko P., Suslov V., Savinkova L., Kolchanov N. How to use SNP_TATA_Comparator to find a significant change in gene expression caused by the regulatory SNP of this gene’s promoter via a change in affinity of the TATAbinding protein for this promoter. Biomed Res Int. 2015;2015:359835. DOI: 10.1155/2015/359835
26. Porto M.S., Pinheiro M.P., Batista V.G., dos Santos R.C., Filho Pde A., de Lima L.M. Plant promoters: an approach of structure and function. Mol Biotechnol. 2014;56(1):38-49. DOI: 10.1007/s12033-013-9713-1 EDN: SPYGUL
27. Pugh B.F. Purification of the human TATA-binding protein, TBP. In: Tymms M.J. (Ed.) In Vitro Transcription and Translation Protocols. (Ser. Methods in Molecular Biology. Vol. 37). Totowa, NJ: Humana Press Inc, 1995;359-367. :359. DOI: 10.1385/0-89603-288-4
28. Rasskazov D., Chadaeva I., Sharypova E., Zolotareva K., Khandaev B., Ponomarenko P., Podkolodnyy N., Tverdokhleb N., Vishnevsky O., Bogomolov A., Podkolodnaya O., Savinkova L., Zemlyanskaya E., Golubyatnikov V., Kolchanov N., Ponomarenko M. Plant_SNP_TATA_Ztester: a Web service that unequivocally estimates the impact of proximal promoter mutations on plant gene expressions. Int J Mol Sci. 2022;23(15):8684. DOI: 10.3390/ijms23158684
29. Rhee H.S., Pugh B.F. Genome-wide structure and organization of eukaryotic pre-initiation complexes. Nature. 2012;483(7389):295-301. DOI: 10.1038/nature10799
30. Sandelin A., Carninci P., Lenhard B., Ponjavic J., Hayashizaki Y., Hume D.A. Mammalian RNA polymerase II core promoters: insights from genomewide studies. Nat Rev Genet. 2007;8:424-436. DOI: 10.1038/nrg2026 EDN: MMEQWN
31. Savinkova L., Drachkova I., Arshinova T., Ponomarenko P., Ponomarenko M., Kolchanov N. An experimental verification of the predicted effects of promoter TATA-box polymorphisms associated with human diseases on interactions between the TATA boxes and TATAbinding protein. PLoS One. 2013;8(2):e54626. DOI: 10.1371/journal.pone.0054626 EDN: RFDWST
32. Senecoff J.F., McKinney E.C., Meagher R.B. De novo purine synthesis in Arabidopsis thaliana. II. The PUR7 gene encoding 5’-phosphoribosyl-4-(N-succinocarboxamide)-5-aminoimidazole synthetase is expressed in rapidly dividing tissues. Plant Physiol. 1996;112(3):905-917. DOI: 10.1104/pp.112.3.905
33. Shahmuradov I.A., Gammerman A.J., Hancock J.M., Bramley P.M., Solovyev V.V. PlantProm: a database of plant promoter sequences. Nucleic Acids Res. 2003;31(1):114-117. DOI: 10.1093/nar/gkg041 EDN: MDFRBL
34. Shannon S., Meeks-Wagner D.R. Genetic interactions that regulate inflorescence development in Arabidopsis. Plant Cell. 1993;5(6):639-655. DOI: 10.1105/tpc.5.6.639
35. Song Y.H., Shim J.S., Kinmonth-Schultz H.A., Imaizumi T. Photoperiodic flowering: time measurement mechanisms in leaves. Annu Rev Plant Biol. 2014;66:441-464. DOI: 10.1146/annurev-arplant-043014-115555
36. Stewart J.J., Stargell L.A. The stability of the TFIIA-TBP-DNA complex dependent on the sequence of the TATAAA element. Biol Chem. 2001;276:30078-30084. DOI: 10.1074/jbc.M105276200
37. Stewart J.J., Fischback J.A., Chen X., Stargell L.A. Non optimal TATA element exibits diverse mechanistic consequences. J Biol Chem. 2006;281:22665-22673. DOI: 10.1074/jbc.M603237200
38. Wobbe C.R., Struhl K. Yeast and human TATA-binding proteins have nearly identical DNA sequence requirements for transcription in vitro. Mol Cell Biol. 1990;10:3859-3867. DOI: 10.1128/MCB.10.8.3859
39. Yamaguchi Y., Itoh Y., Takeda Y., Yamazaki K. TATA sequence requirements for the initiation of transcription for an RNA polymerase II in vitro transcription system from Nicotiana tabacum. Plant Mol Biol. 1998;38(6):1247-1252. :1006056128129. DOI: 10.1023/a
Выпуск
Другие статьи выпуска
Критерий Стьюдента статистической значимости разности средних двух выборок, предложенный Р. Фишером в1925 г., до сих пор является одним из самых востребованных методов статистического анализа. За почти столетие его использования сложилась устойчивая система рекомендаций и условий его применения, которая изложена в учебниках и руководствах по статистической обработке данных. Как правило, настоятельно требуется предварительная проверка нормальности распределения исходных выборок и равенства их дисперсий. В случае ненормальности рекомендуется использовать непараметрические методы, например критерий Манна-Уитни. В работе представлена более современная точка зрения на эту проблему, обусловленная несколькими взаимосвязанными причинами. Во-первых, за прошедшее столетие накоплен значительный практический опыт применения t -критерия Стьюдента, который заставляет сильно сомневаться в обязательности проверки нормальности и равенства дисперсий, а также применения ранговых критериев в случае отсутствия нормальности. Во-вторых, теория тоже не стояла на месте. Появились расчет критерия Стьюдента через точечно-бисериальный коэффициент корреляции и альтернативы методам «нормальной теории» в виде свободных от распределения процедур. В-третьих, кардинально выросли вычислительные возможности, позволяющие без дополнительных предположений моделировать в компьютере генеральные распределения исходных выборок и по ним оценивать требуемые p -value.
Исследован половой полиморфизм Geranium sylvaticum L. в двух популяциях в луговом и лесном фитоценозах подтаежного правобережья Оби (окрестности г. Новосибирска). В зависимости от комбинации обоеполых, пестичных и частично андростерильных цветков обнаружены три половых фенотипа: гермафродитный, женский и гиномоноэцичный. У ряда гермафродитных фенотипов формируются частично андростерильные цветки, среди которых преобладают цветки с 5 стаминодиями и 5 нормальными тычинками. Частично андростерильные цветки малочисленны и образуются в верхней и/или нижней части соцветия в начале и/или конце цветения растений. Гиномоноэцичные фенотипы представлены в двух вариантах: женский фенотип с единичными частично андростерильными цветками и гермафродитный фенотип с несколькими пестичными цветками. Женские фенотипы образуют приблизительно в 2 раза меньше цветков и в 1.6 раза меньше плодов, чем гермафродитные (различия статистически значимы), однако образование плодов в расчете на цветок у женских фенотипов в 1.4 раза выше, чем у гермафродитных. В условиях низкой освещенности гермафродитные фенотипы с частично андростерильными цветками встречаются в 2.2 раза чаще, чем при высоком уровне освещения. Соотношение двух форм гермафродитных фенотипов (с частично андростерильными цветками и без них) в луговом и лесном фитоценозах различается статистически значимо ( p = 0.0247 < 0.05). При высоком уровне освещения гермафродитные фенотипы продуцируют в 1.6 раза больше плодов, чем при низком; различия статистически значимы ( p < 0.05). В исследуемых популяциях G. sylvaticum выявлена низкая доля женских фенотипов как в луговом, так и в лесном фитоценозах: 7.1 и 4.7 % соответственно. Гиномоноэцичные фенотипы в популяциях отмечаются единично -0.8-1.6 %. Для G. sylvaticum характерна сравнительно низкая встречаемость женских и гиномоноэцичных фенотипов и заметная доля гермафродитных с частично андростерильными цветками в европейской и азиатской частях ареала вида.
Полувековая жизнь в науке Л. П. Осиповой была тесно связана со становлением, организацией и развитием комплексных и широкомасштабных исследований генетической структуры популяций человека Северной Евразии. Были инициированы и проводились исследования в различных направлениях популяционной и эволюционной генетики человека, молекулярной генетики и иммуногенетики, демографии и биомедицины коренных народов; изучались механизмы адаптации человека к факторам окружающей среды, а также влияние техногенных факторов на окружающую среду и на здоровье человека. Совокупность результатов масштабных геномных исследований международных консорциумов с участием коллектива Л. П. Осиповой позволила реконструировать предковые геномы и воссоздать пути миграции человека в историческом прошлом.
Целью данной работы была идентификация полиморфных локусов в геномах Daphnia с помощью анализа последовательности генома и экспериментального анализа реальных образцов, собранных в естественных условиях. Мы использовали праймеры, предсказанные алгоритмом амплификации ДНК из образцов дафний, и капиллярный электрофорез для выявления полиморфных локусов. Это сделано для детекции полиморфных локусов в результате единственного эксперимента, когда наличие полиморфизмов с частотой, достаточной для генетических исследований, детектируется как появление множественных пиков на электрофореграмме. Таким образом, мы оценивали эффективность метода капиллярного электрофореза и уточняли параметры популяции, включая долю полового размножения и эффективную численность популяции. Изучение полиморфных локусов становится особенно актуальным в контексте изменения климата и усиления антропогенного воздействия на экосистемы, поскольку эти факторы могут существенно влиять на генетическое разнообразие и адаптацию популяций. Полиморфные локусы, содержащие микросателлитные повторы, могут служить индикаторами генетической стабильности и способности видов адаптироваться к изменяющимся условиям окружающей среды. В условиях глобального изменения климата и усиливающегося антропогенного воздействия, такого как загрязнение окружающей среды, урбанизация и изменения ландшафта, гидробионты сталкиваются с новыми вызовами, требующими быстрой адаптации. Полиморфные локусы, благодаря своей высокой изменчивости, могут предоставить ценную информацию о генетической структуре популяций и их потенциале к адаптации. В контексте наших исследований изучение полиморфных локусов у Daphnia приобретает особую важность, учитывая их экологическую роль и чувствительность к изменениям окружающей среды. Представители рода Daphnia как ключевые компоненты пресноводных экосистем могут служить модельными организмами для изучения генетической адаптации к изменению климата и антропогенным воздействиям. Понимание полиморфных локусов у Daphnia может дать ценные данные для оценки генетической стабильности и адаптивного потенциала этих популяций, что особенно важно в условиях быстро меняющихся условий окружающей среды.
Признаки, связанные с весом тела в разном возрасте, хорошо коррелируют с продуктивностью, здоровьем и продолжительностью хозяйственного использования крупного рогатого скота. В то же время у крупного рогатого скота вес тела - признак с высокой наследуемостью. Полногеномный анализ ассоциаций позволяет найти генетические варианты и потенциальные гены-кандидаты, контролирующие интересующий признак. Однако обзоры работ по изучению веса тела с помощью полногеномного анализа ассоциаций у животных молочных пород крупного рогатого скота практически отсутствуют. Целью этой работы было выявление потенциальных генов-кандидатов, ассоциированных с признаками веса тела, у животных молочных пород крупного рогатого скота на основании исследований по полногеномному анализу ассоциаций. Поиск литературы проведен с использованием поискового запроса “Cattle AND Dairy AND Weight AND Genome-wide AND Association AND Study”. Критерием для включения публикации в нашу работу служила идентификация хотя бы одного гена-кандидата, достоверно ассоциированного с признаком, связанным с весом тела у животных молочной породы крупного рогатого скота. Количество пересечений между списками генов-кандидатов подсчитывали с помощью программы Venn. Анализ взаимодействий между генами/белками проводили с использованием веб-ресурса GeneMANIA; перепредставленные термины генной онтологии были найдены с помощью веб-инструмента DAVID. Было обнаружено 20 генов, ассоциированных в одной публикации с разными признаками веса либо с одинаковым признаком, но в нескольких публикациях. Среди них наибольшее количество пересечений имели гены TNNT3, DYRK4, AKAP3, GALNT8, NDUFA9 и KCNA1. Общие биохимические пути и белок-белковые взаимодействия были найдены для пар генов TNNT3-TNNI2 и FGF6-FGF23. Общие белковые домены были обнаружены у пар TNNT3 - TNNI2, FGF6 - FGF2 3 и KCNA1 - KCNA6. При функциональной аннотации вышеупомянутого списка из 20 генов были выявлены перепредставленные термины генной онтологии, указывающие на обогащение списка генами, кодирующими белки комплекса тропонина ( TNNT3 и TNNI2 ), белки калиевых каналов внутреннего выпрямления ( KCNA1 и KCNA6 ), а также белки-рецепторы фактора роста фибробластов ( FGF6 и FGF23 ).
Статистика статьи
Статистика просмотров за 2025 год.
Издательство
- Издательство
- НИИТПМ
- Регион
- Россия, Новосибирск
- Почтовый адрес
- 630089, г. Новосибирск, ул. Б. Богаткова, 175/1, Метро "Золотая нива", Автобус "Молодежная, Кошурникова"
- Юр. адрес
- 630090, г. Новосибирск, пр-т Академика Лаврентьева, 10
- ФИО
- Рагино Юлия Игоревна (Руководитель)
- Контактный телефон
- +7 (383) 3730981
- Сайт
- https://iimed.ru/